Ich werde Single-Cell-RNA-Seq-Analyse durchführen und Zelltyp-Annotation vornehmen
Bioinformatik-Pipeline-Entwickler
Über diesen Service
Hast du Single-Cell-RNA-Seq-Daten, die eine professionelle Analyse und Zelltyp-Identifikation benötigen?
Ich werde dein scRNA-seq-Datensatz mit Seurat analysieren
und eine vollständige Zelltyp-Annotation mit
publikationsfertigen Visualisierungen liefern.
WAS DU BEKOMMST:
- Qualitätskontrolle und Filterung von Zellen mit niedriger Qualität
- Normalisierung und Skalierung
- PCA-Dimensionenreduktion
- Graph-basierte Clusterbildung
- UMAP-Visualisierung
- Marker-Gen-Identifikation pro Cluster
- Biologische Zelltyp-Annotation
- Vollständiger Analysebericht
MEINE ERFAHRUNG:
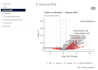
Ich habe 2700 menschliche PBMCs analysiert und 9 unterschiedliche
Zellpopulationen identifiziert, darunter T-Zellen, B-Zellen, NK-Zellen,
Monozyten, Dendritische Zellen und Thrombozyten, mit Seurat.
Vollständiger Pipeline auf GitHub verfügbar.
WAS ICH VON DIR BRAUCHE:
- 10X Genomics-Ausgabedateien (Barcodes, Features, Matrix)
ODER verarbeitete Count-Matrix
- Organismenname (Mensch, Maus usw.)
- Jegliche bekannte Biologie deines Samples
TOOLS: R, Seurat, ggplot2, dplyr, UMAP,
PCA, Git, Linux
Sende mir vor der Bestellung eine Nachricht, um dein Dataset zu besprechen
Ich werde die Machbarkeit zuerst bestätigen.
Expertise:
Klassifizierung
•
Clustering
•
Prädiktive Analyse
Programmiersprache:
Python
•
R
Frameworks:
Panda
APIs:
Andere
Tools:
Jupyter-Notizbuch
•
Colab