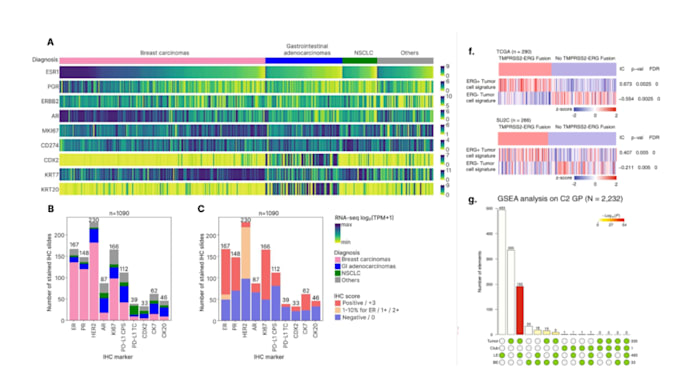
Ich werde jede bioinformatische und maschinelles Lernen Analyse durchführen
Bioinformatik NGS scRNA seq Multiomics Machine Learning
Über diesen Service
Hallo, ich bin Sheraz, ein Bioinformatik-Forscher und Computational Biologist. Ich spezialisiere mich auf fortgeschrittene bioinformatische und maschinelles Lernen Analysen für Forscher, Studenten und Organisationen. Ich helfe dabei, komplexe biologische Datensätze in klare, umsetzbare Erkenntnisse umzuwandeln.
Mit diesem Gig biete ich maßgeschneiderte Lösungen für eine Vielzahl biologischer Daten, einschließlich NGS (WGS, WES), RNA-seq, scRNA-seq, CNV-Analyse, Krebsgenomik und Multi-Omics-Datensätze. Ich implementiere auch maschinelles Lernen und KI-basierte Modelle für prädiktive Analysen und Klassifizierungsaufgaben.
Meine Dienstleistungen umfassen:
- Datenvorverarbeitung & QC: Reinigung, Normalisierung und Ausrichtung
- Statistische Analyse: Differentielle Expression, Merkmalsauswahl und Modellierung
- Maschinelles Lernen & KI: Prädiktive Modellierung, Clustering, Klassifikation und Deep Learning
- Visualisierung: PCA, Heatmaps, Volcano-Plots, Netzwerk- und Wegdiagramme
- Detaillierte Berichte: Klare, publikationsreife Ergebnisse mit biologischer Interpretation
Ob du grundlegende bioinformatische Analyse oder fortgeschrittene ML-Pipelines benötigst, ich liefere präzise, reproduzierbare und forschungswürdige Ergebnisse, die auf dein Projekt zugeschnitten sind.
Lass uns deine Rohdaten in bedeutende Entdeckungen verwandeln!
Mein Portfolio
FAQ
Automatische Übersetzung
Welche Arten von bioinformatischen Daten analysierst du?
Ich analysiere NGS-Datensätze (WGS, WES, RNA-seq, scRNA-seq), CNV-Daten, Krebsgenomik und andere Multi-Omics-Datensätze. Ich arbeite auch mit benutzerdefinierten biologischen Datensätzen für maschinelles Lernen.
Bietest du maschinelles Lernen oder KI-basierte Analysen für biologische Daten an?
Ja! Ich implementiere Modelle des maschinellen Lernens, Deep-Learning-Pipelines, Clustering, Klassifikation und prädiktive Analysen auf bioinformatischen und genomischen Datensätzen.
Kannst du Rohsequenzierungsdaten verarbeiten?
Absolut. Ich führe Rohdatenvorverarbeitung, Qualitätskontrolle, Trimmen, Ausrichtung und Normalisierung durch, um saubere, publikationsreife Ergebnisse zu gewährleisten.
Wirst du Visualisierungen und Berichte liefern?
Ja, ich liefere publikationswürdige Visualisierungen wie PCA, Heatmaps, Volcano-Plots und Netzwerk- bzw. Wegdiagramme, zusammen mit einem detaillierten Bericht mit biologischer Interpretation.
Bietest du Beratung oder Unterstützung für mein Projekt an?
Ja, ich biete fachkundige bioinformatische und maschinelles Lernen Beratung an und leite dich bei Datenhandling, Analyse-Strategien und der Interpretation der Ergebnisse an.
Kannst du an Single-Cell-RNA-seq- oder Multi-Omics-Projekten arbeiten?
Absolut. Ich spezialisiere mich auf Single-Cell-RNA-seq (scRNA-seq), Multi-Omics-Integration und fortgeschrittene genomische Analysen mit Modellen des maschinellen Lernens.
Welche Software und Tools nutzt du für die Analyse?
Ich verwende Python, R, Linux, Bash, DESeq2, EdgeR, scikit-learn, TensorFlow, PyTorch und andere bioinformatische sowie ML-Tools, um zuverlässige, reproduzierbare Ergebnisse zu liefern.